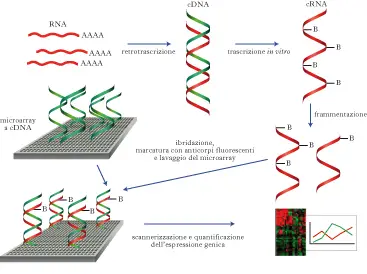
Come ottenere una libreria genomica
Per avere una libreria genomica:
- si spezzetta
- clonato
- amplificato
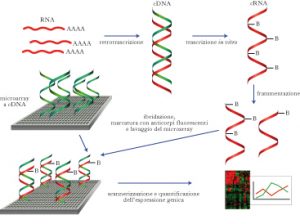
Scrinazione molecolare o biochimica
Una volta avuto a disposizione questo materiale possiamo scrinarlo o caratterizzarlo sia con metodi molecolari che biochimici.
Un metodo molto interessante per scrinare una libreria si può usare uno sceening per complementazione.
Scenning per complementazione
Questo metodo è attuabile solo quando abbiamo a disposizione una mutazione o un ceppo mutante quando un fenotipo può essere ripristinato da un clone wildtype presente nella libreria che vogliamo studiare.
Per esempio un ceppo di lievito non in grado di sintetizzare il triptofano viene trasformato con la libreria a disposizione e seminando il prodotto della trasformazione su un terreno contenente triptofano, se si formano colonie, vuol dire che il mio lievito ha acquisito dalla libreria il gene che gli serviva.
Digerendo il Dna genomico trovo una serie di frammenti con peso molecolare molto vicino e si forma uno smiar cioè non vedo bande nette, se la digestione non fosse completa invece di questo smiar avrò una banda di dna genomico che rimane in alto.
La presenza di un osmiar uniforme mi dice che la digestione è corretta.
A questo punto questi frammenti possono essere inseriti all’interno di un vettore fagico, la presenza dei siti così mi permette un corretto impacchettamento del frammento all’interno della particella fagica che utilizzero per infettare la cellula ospite.
C’è un metodo relativamente nuovo (2006).
Librerie genomiche
Si parte dal dna genomico frammentato, si legano adattatori che stabilizzano questi frammenti e legati primer chimati primer universali.
A questo punto viene clonato all’interno di eppendorf con la tecnologia emulsion PCR perchè all’interno di queste provette c’è un’emulsione acqua/olio che creano dei microambienti.
Invece di avere tutto mescolato insieme si creano dei microambienti in cui praticamente una sferetta si trova in corrispondenza di una sola molecola di DNA al quale si lega.
Queste sferette per affinità vengono posizionate all’interno di pozzetti di una piastra.
Opero poi una reazione di sequenziamento su queste sferette che hanno ancorata questa molecola di DNA.
Per sequenziare il filamento posso usare vari metodi, per esempio usare un primer che poi da via a polimerizzazione, con vari nucleotidi marcati.
Altrimenti il “metodo per ligazione”, mentre nel primo metodo era un metodo di Sanger, in questo caso, dopo che si è attaccato un primer chiamato ancora, non si attacca un nucleotide per volta ma uno stretch oligonucleotidico marcato ogni volta in maniera diverso.
La cosa buona di questo metodo è che dopo aver posizionato i frammenti di dna genomico noi possiamo sequenziarli subito.