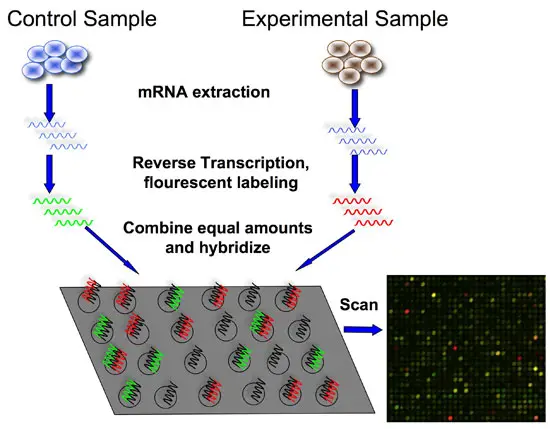
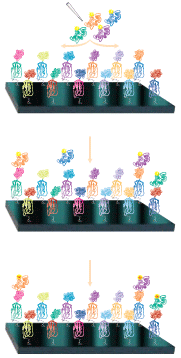• Le sequenze nucleotidiche sono spottate. • La loro lunghezza è di 25 basi. • Non si usa una sola sonda per spot;
Archivio Autore: Marco
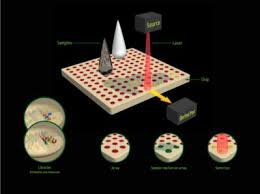
Si usano dei nanochip, cioè l'area dove si lega la proteina è nell'ordine dei nanometri. Per valutare i segnali si usa la microscopia a forza atomica. Il vantaggio di questa tecnica è che riduco i reagenti da usare e tutti i materiali di prima necessità. I problemi di queste tecniche • difficoltà della rapida identificazione […]
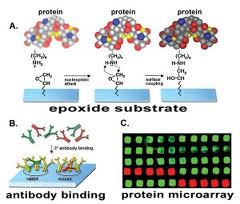
Ciascuna posizione del vetrino è occupata da una proteina. 1. Le proteine native sono spottate sul vetrino 2. Aggiungo una proteina X 3. spottate proteine native + alcune proteine legate alla proteina X La proteina X è semrpe marcata con un fluorocromo o rilevabile tramite test della fosfatasi. Della proteina X conosco la sequenza ma […]
Produce una quantità enorme di informazioni. In due estratti cellulari (A/B) dovrò marcarli con due molecole diverse. Nella pratica le proteine di A e B competeranno per arrivare a legarsi al ligando. Ottengo 3 spot diversi: • Spot verde: si è legato A • Spot Rosso: si è legato B • Spot Giallo: sia A […]
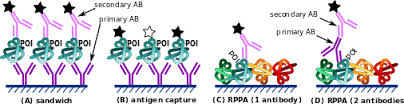
I microarray di proteine, sono strumenti utili per molte applicazioni della proteomica. Le piastre in nitrato di cellulosa sono il miglior substrato possibile per microarray di proteine, ad esempio gli array proteici diretti ed i microarray proteici in fase inversa. La molteplicità degli spot proteici evidenziati sulla superficie della piastra permettono la visione simultanea di […]
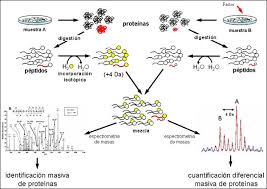
Lo studio del proteoma (tutte le proteine di un organismo). vuol dire conoscere: • le proteine che sono presenti • definire la loro struttura • studiare le interazioni di queste proteine • come si possono correlarle con la genomica Il proteoma è un'entità dinamica, perchè cambia continuamente all'interno del solito microrganismo.
studiare dal punto di vista ecologico gli ambienti estremi dove ci sono microrganismi. Es.a Richmond c'è un ambiente acido e la comunità di microrganismi forma un biofilm (di colore rosato). Inoltre trovati altri nanorganismi (appartenenti agli archea con estroflessioni particolari). Un'altra zona è il mar dei Sargassi dove crescono le alghe in vere aree giganti […]
La scoperta di piccole molecole tramite la metagenomica funzionale è concentrata su antibiotici per le applicazioni farmaceutiche e per il loro ruolo nell'ecosistema. Gli antibiotici tradizionalmente scrinati sono da molecole che inbiscono la crescita batterica a antibiotici delle librerie metagenomiche.
La frequenza dei cloni metagenomici che esprimono una qualche attività è bassa. Per esempio nella ricerca di cloni lipolitici derivati dal German soil, soltanto 1 su 730 mila cloni mostra attività. La scarsità dell'attività dei cloni necessita perciò di uno sviluppo di uno screening efficiente e di una selezione per scoprire nuove molecole o attività.
Tutto è partito dalla produzione di una libreria di mutanti random prodotta utilizzando un trasposone. Per produrla si usano trasposoni della famiglia TN10. In un plasmide è presente questo trasposone che ha sequenze "IS" al 3' ed al 5', al suo interno c'è una cassetta che codifica per una proteina che da resistenza alla spectinomicina. […]